
园艺学报 ›› 2026, Vol. 53 ›› Issue (3): 683-696.doi: 10.16420/j.issn.0513-353x.2025-0310
陈钰珊1,2,*, 高欢1,2,*, 吴俊康1,2, 王莉梅1,2, 黄春辉1,2, 徐小彪1,2,**( ), 廖光联1,2,**(
), 廖光联1,2,**( )
)
收稿日期:2025-07-02
修回日期:2025-09-28
出版日期:2026-03-25
发布日期:2026-03-20
通讯作者:
作者简介:* 共同第一作者
基金资助:
CHEN Yushan1,2, GAO Huan1,2, WU Junkang1,2, WANG Limei1,2, HUANG Chunhui1,2, XU Xiaobiao1,2,**( ), LIAO Guanglian1,2,**(
), LIAO Guanglian1,2,**( )
)
Received:2025-07-02
Revised:2025-09-28
Published:2026-03-25
Online:2026-03-20
摘要:
为解析毛花猕猴桃(Actinidia eriantha)β-淀粉酶(β-amylase,BAM)基因家族信息,基于毛花猕猴桃‘赣绿1号’高质量参考基因组数据(PRJNA839193),鉴定了AeBAM家族成员并对其理化性质、进化关系进行了分析,同时利用转录组和qRT-PCR技术明确了AeBAM在不同组织及果实发育后期(淀粉降解期)的表达特征。在毛花猕猴桃中共鉴定出17个AeBAM成员,编码氨基酸数量在189 ~ 751之间、理论等电点5.24 ~ 10.01、分子量21 149.85 ~ 84 142.08 Da。根据多物种进化树分析,BAM可以分为5个亚族,其中I和V亚族成员居多;共线性分析表明,AeBAM家族内部共存在10对复制基因对和5对串联重复基因对,所有成员的Ka/Ks比值均小于1,在进化过程中受到纯化选择;AeBAM家族基因启动子上含有大量的光响应、逆境胁迫和激素调控相关的顺式作用元件。转录组分析表明,AeBAM成员表达具有组织特异性,其中AeBAM5、AeBAM13和AeBAM16在果实中具有较高的表达量且在果实套袋后表达量显著上升;qRT-PCR表明,AeBAM5和AeBAM13表达量在淀粉降解期显著上升并与淀粉降解负相关,可被认为是调控果实淀粉降解的关键基因家族成员。
陈钰珊, 高欢, 吴俊康, 王莉梅, 黄春辉, 徐小彪, 廖光联. 毛花猕猴桃AeBAM基因家族鉴定及其表达分析[J]. 园艺学报, 2026, 53(3): 683-696.
CHEN Yushan, GAO Huan, WU Junkang, WANG Limei, HUANG Chunhui, XU Xiaobiao, LIAO Guanglian. Identification and Expression Analysis of AeBAM Gene Family in Actinidia eriantha[J]. Acta Horticulturae Sinica, 2026, 53(3): 683-696.
| 基因 Gene | 上游引物序列(5′-3′) Forward primer sequences | 下游引物序列(5′-3′) Revers primer sequences | 产物大小/bp Product |
|---|---|---|---|
| AeBAM1 | GAATGGCTACAAGAGGCT | TATGTCGGGATTGCTACG | 157 |
| AeBAM2 | GGAGGAAGGCTATGTGGG | TCCGTGTAGGCAAGGTCA | 283 |
| AeBAM3 | TTTGTGCCCACTTTATCC | CAACCTCTTGTAGCCATT | 384 |
| AeBAM4 | TACGCTATCCCTCTTATCC | ATTTCTGCCGCTTTCTTC | 109 |
| AeBAM5 | TTTCCTTGGGTTGTGATT | GTCTTTCTTTCCGATTGC | 281 |
| AeBAM6 | AGGGATGTTGCTTCTTCA | GGTTCATCTGCTGCTCATT | 266 |
| AeBAM7 | CCCGATGGCACTACCTAT | GCACCCTGGAACCAACAT | 298 |
| AeBAM8 | GATTCACTGGCACTACGGG | GGGCATCCTGAGGCTGTT | 173 |
| AeBAM9 | GCCGATTGATGGAGTAAG | GATGCGTGGAAGCAGAGC | 264 |
| AeBAM10 | GGCAAGGTGGTGTCAGTC | CATCCGATTTCCAGTTTT | 103 |
| AeBAM11 | AGAAGGGAAGCCTCAGTG | GTTAGTTCAGCAGGGTGT | 297 |
| AeBAM12 | TCAAGGATTGGCTGTGGC | GATGACGGCTGTTGATGC | 141 |
| AeBAM13 | AGTGCGGAGGAAATGTTGG | TCTAAGCACTGGTAACGAAT | 158 |
| AeBAM14 | GTGCGGAGGAAATGTTGG | AAGGATAGGTATTCGGCATT | 129 |
| AeBAM15 | AGTGCGGAGGAAATGTTGG | GCCAAGGATAGGTATTCGGG | 133 |
| AeBAM16 | TGGAACAATGATTACGGACAA | GTAGTGCCAATGAATCCCTG | 150 |
| AeBAM17 | ATCTGATTCCAGGGTGCC | CATTCATTGTTCGTGGCTTG | 89 |
表1 qRT-PCR引物序列
Table 1 qRT-PCR primer sequences
| 基因 Gene | 上游引物序列(5′-3′) Forward primer sequences | 下游引物序列(5′-3′) Revers primer sequences | 产物大小/bp Product |
|---|---|---|---|
| AeBAM1 | GAATGGCTACAAGAGGCT | TATGTCGGGATTGCTACG | 157 |
| AeBAM2 | GGAGGAAGGCTATGTGGG | TCCGTGTAGGCAAGGTCA | 283 |
| AeBAM3 | TTTGTGCCCACTTTATCC | CAACCTCTTGTAGCCATT | 384 |
| AeBAM4 | TACGCTATCCCTCTTATCC | ATTTCTGCCGCTTTCTTC | 109 |
| AeBAM5 | TTTCCTTGGGTTGTGATT | GTCTTTCTTTCCGATTGC | 281 |
| AeBAM6 | AGGGATGTTGCTTCTTCA | GGTTCATCTGCTGCTCATT | 266 |
| AeBAM7 | CCCGATGGCACTACCTAT | GCACCCTGGAACCAACAT | 298 |
| AeBAM8 | GATTCACTGGCACTACGGG | GGGCATCCTGAGGCTGTT | 173 |
| AeBAM9 | GCCGATTGATGGAGTAAG | GATGCGTGGAAGCAGAGC | 264 |
| AeBAM10 | GGCAAGGTGGTGTCAGTC | CATCCGATTTCCAGTTTT | 103 |
| AeBAM11 | AGAAGGGAAGCCTCAGTG | GTTAGTTCAGCAGGGTGT | 297 |
| AeBAM12 | TCAAGGATTGGCTGTGGC | GATGACGGCTGTTGATGC | 141 |
| AeBAM13 | AGTGCGGAGGAAATGTTGG | TCTAAGCACTGGTAACGAAT | 158 |
| AeBAM14 | GTGCGGAGGAAATGTTGG | AAGGATAGGTATTCGGCATT | 129 |
| AeBAM15 | AGTGCGGAGGAAATGTTGG | GCCAAGGATAGGTATTCGGG | 133 |
| AeBAM16 | TGGAACAATGATTACGGACAA | GTAGTGCCAATGAATCCCTG | 150 |
| AeBAM17 | ATCTGATTCCAGGGTGCC | CATTCATTGTTCGTGGCTTG | 89 |
| 基因名 Gene name | 基因ID Gene ID | 氨基酸数 No. of amino acid | 分子量/Da Molecular weight | 等电点 pI | 稳定系数 Instability index | 脂溶指数 Aliphatic index | 亲水性 Hydrop- athicity | 已报道同源基因 Reported homologous genes |
|---|---|---|---|---|---|---|---|---|
| AeBAM1 | Chr02G799 | 751 | 84 142.08 | 5.82 | 34.45 | 77.75 | -0.35 | / |
| AeBAM2 | Chr02G1164 | 568 | 63 467.87 | 5.57 | 40.59 | 68.89 | -0.45 | / |
| AeBAM3 | Chr06G622 | 700 | 78 501.26 | 5.24 | 38.18 | 73.40 | -0.46 | / |
| AeBAM4 | Chr06G623 | 556 | 63 133.23 | 5.65 | 37.67 | 74.69 | -0.39 | / |
| AeBAM5 | Chr11G331 | 480 | 54 004.19 | 8.29 | 33.44 | 67.25 | -0.53 | AdBAM3L(Acc28966); AcBAM5(Actinidia10870.t1) |
| AeBAM6 | Chr11G561 | 541 | 60 915.04 | 6.65 | 37.90 | 67.80 | -0.31 | / |
| AeBAM7 | Chr11G638 | 666 | 74 694.92 | 5.89 | 39.40 | 70.33 | -0.45 | / |
| AeBAM8 | Chr13G233 | 564 | 62 786.18 | 5.90 | 45.97 | 70.27 | -0.42 | / |
| AeBAM9 | Chr16G812 | 532 | 58 600.29 | 6.18 | 28.35 | 81.73 | -0.26 | AcBAM13(Actinidia00051.t1) |
| AeBAM10 | Chr16G1012 | 189 | 21 149.85 | 10.01 | 44.29 | 111.43 | 0.17 | / |
| AeBAM11 | Chr19G603 | 523 | 59 697.34 | 8.93 | 51.50 | 80.38 | -0.30 | / |
| AeBAM12 | Chr20G1070 | 645 | 72 789.04 | 6.20 | 41.02 | 71.21 | -0.48 | / |
| AeBAM13 | Chr22G622 | 547 | 61 739.99 | 8.62 | 38.39 | 66.54 | -0.53 | AdBAM3.1(Acc15874) |
| AeBAM14 | Chr23G1204 | 501 | 56 841.28 | 8.24 | 37.43 | 67.19 | -0.58 | / |
| AeBAM15 | Chr23G1205 | 301 | 34 345.80 | 8.96 | 40.58 | 82.23 | -0.34 | / |
| AeBAM16 | Chr23G1206 | 501 | 56 428.79 | 8.00 | 37.67 | 66.99 | -0.56 | / |
| AeBAM17 | Chr25G384 | 546 | 61 462.78 | 8.58 | 36.62 | 70.57 | -0.51 | AdBAM3(Acc16695) |
表2 毛花猕猴桃AeBAM成员编码蛋白的理化性质
Table 2 Protein physical and chemical properties analysis of AeBAM
| 基因名 Gene name | 基因ID Gene ID | 氨基酸数 No. of amino acid | 分子量/Da Molecular weight | 等电点 pI | 稳定系数 Instability index | 脂溶指数 Aliphatic index | 亲水性 Hydrop- athicity | 已报道同源基因 Reported homologous genes |
|---|---|---|---|---|---|---|---|---|
| AeBAM1 | Chr02G799 | 751 | 84 142.08 | 5.82 | 34.45 | 77.75 | -0.35 | / |
| AeBAM2 | Chr02G1164 | 568 | 63 467.87 | 5.57 | 40.59 | 68.89 | -0.45 | / |
| AeBAM3 | Chr06G622 | 700 | 78 501.26 | 5.24 | 38.18 | 73.40 | -0.46 | / |
| AeBAM4 | Chr06G623 | 556 | 63 133.23 | 5.65 | 37.67 | 74.69 | -0.39 | / |
| AeBAM5 | Chr11G331 | 480 | 54 004.19 | 8.29 | 33.44 | 67.25 | -0.53 | AdBAM3L(Acc28966); AcBAM5(Actinidia10870.t1) |
| AeBAM6 | Chr11G561 | 541 | 60 915.04 | 6.65 | 37.90 | 67.80 | -0.31 | / |
| AeBAM7 | Chr11G638 | 666 | 74 694.92 | 5.89 | 39.40 | 70.33 | -0.45 | / |
| AeBAM8 | Chr13G233 | 564 | 62 786.18 | 5.90 | 45.97 | 70.27 | -0.42 | / |
| AeBAM9 | Chr16G812 | 532 | 58 600.29 | 6.18 | 28.35 | 81.73 | -0.26 | AcBAM13(Actinidia00051.t1) |
| AeBAM10 | Chr16G1012 | 189 | 21 149.85 | 10.01 | 44.29 | 111.43 | 0.17 | / |
| AeBAM11 | Chr19G603 | 523 | 59 697.34 | 8.93 | 51.50 | 80.38 | -0.30 | / |
| AeBAM12 | Chr20G1070 | 645 | 72 789.04 | 6.20 | 41.02 | 71.21 | -0.48 | / |
| AeBAM13 | Chr22G622 | 547 | 61 739.99 | 8.62 | 38.39 | 66.54 | -0.53 | AdBAM3.1(Acc15874) |
| AeBAM14 | Chr23G1204 | 501 | 56 841.28 | 8.24 | 37.43 | 67.19 | -0.58 | / |
| AeBAM15 | Chr23G1205 | 301 | 34 345.80 | 8.96 | 40.58 | 82.23 | -0.34 | / |
| AeBAM16 | Chr23G1206 | 501 | 56 428.79 | 8.00 | 37.67 | 66.99 | -0.56 | / |
| AeBAM17 | Chr25G384 | 546 | 61 462.78 | 8.58 | 36.62 | 70.57 | -0.51 | AdBAM3(Acc16695) |

图2 AeBAM家族基因共线性与Ka/Ks分析 A:AeBAM家族成员内部共线性分析;B:AeBAM家族成员Ka/Ks分析;C:多物种BAM家族成员间共线性分析
Fig. 2 Collinearity and Ka/Ks analysis of AeBAM gene family members A:Collinearity analysis among AeBAM family members;B:Ka/Ks analysis of AeBAM family members;C:Collinearity analysis of BAM family members across multiple species
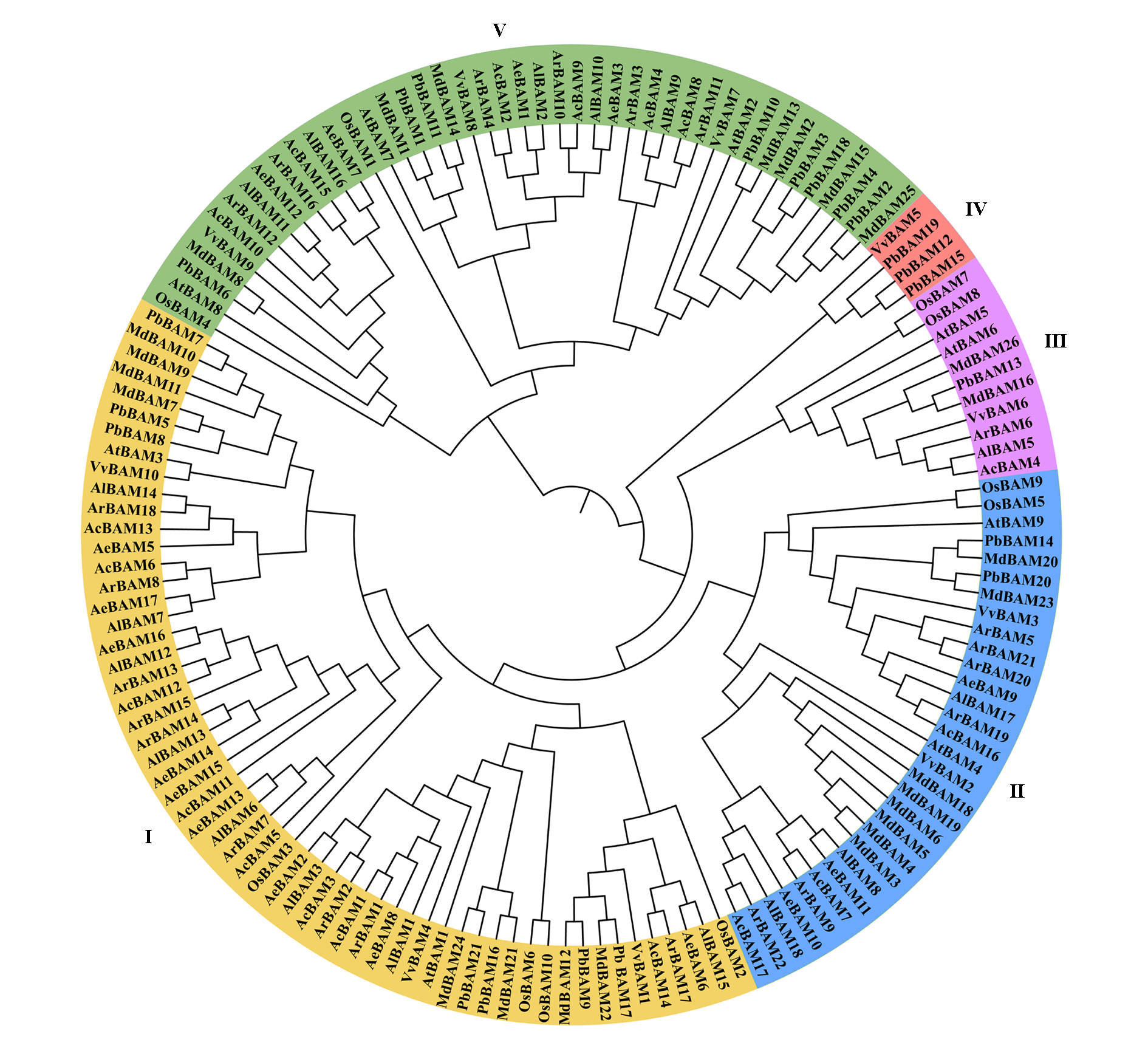
图3 毛花猕猴桃和多个物种的BAM家族基因系统进化树分析 Ac:中华猕猴桃;Ae:毛花猕猴桃;Al:阔叶猕猴桃;Ar:山梨猕猴桃;At:拟南芥;;Md:苹果;Os:水稻;Pb:梨;Vv:葡萄
Fig. 3 Phylogenetic tree analysis of BAM between Actinidia eriantha and other species Ac:Actinidia chinensis;Ae:Actinidia eriantha;Al:Actinidia latifolia;Ar:Actinidia rufa;At:Arabidopsis thaliana;Md:Malus domestica;Os:Oryza sativa;Pb:Pyrus bretschneideri;Vv:Vitis vinifera
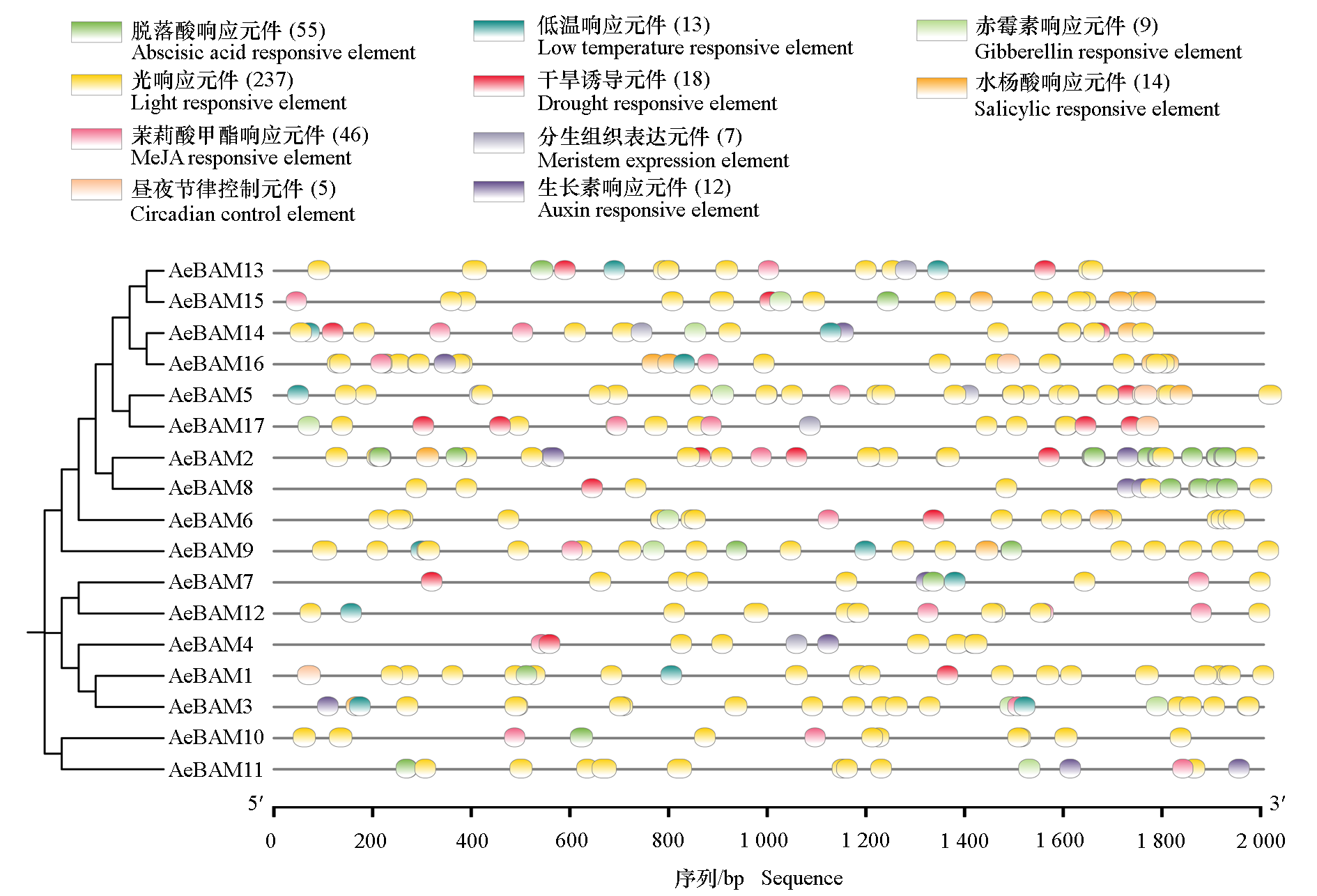
图4 毛花猕猴桃AeBAM家族基因启动子顺式作用元件分析 括号中为各顺式元件的数量
Fig. 4 cis-Acting elements analysis of AeBAM gene promoter Numbers in parentheses indicate the count of each cis-acting element
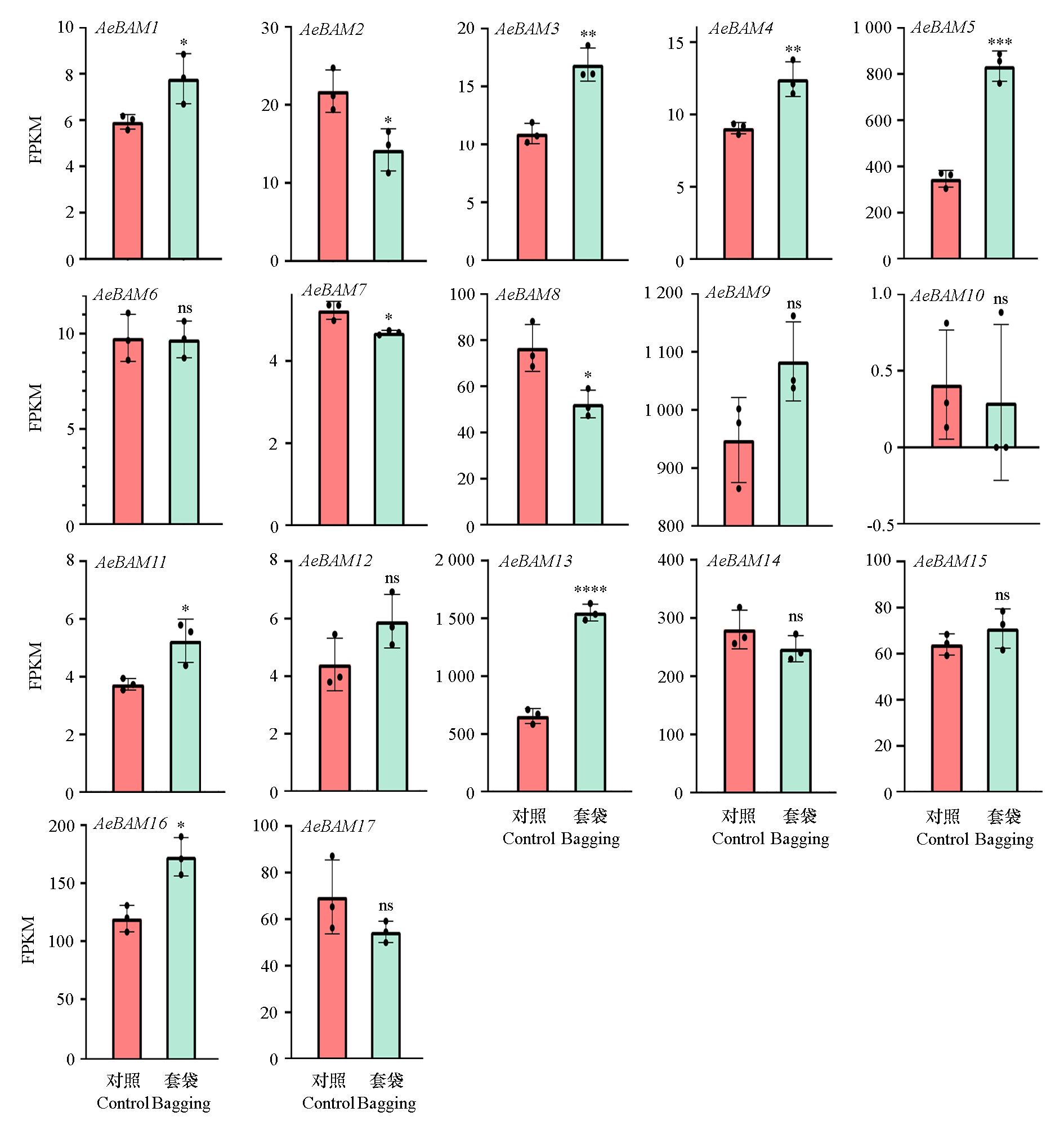
图6 毛花猕猴桃果实套袋后AeBAM家族基因的表达量 * 表示在P < 0.05水平具有显著性差异,** 表示在P < 0.01水平具有显著性差异,*** 表示在P < 0.001水平具有显著性差异,**** 表示在P < 0.0001水平具有显著性差异,ns 表示无显著差异
Fig. 6 Expression analysis of AeBAM family genes after fruit bagging * indicates significant differences at P < 0.05,** indicates significant differences at P < 0.01,*** indicates significant differences at P < 0.001,**** indicates significant differences at P < 0.0001,ns indicates no significant difference
| [1] |
|
| [2] |
doi: 10.1016/j.molp.2023.09.010 URL |
| [3] |
doi: 10.16420/j.issn.0513-353x.2024-0373 |
|
陈敏氡, 王彬, 白昌辉, 裘波音, 刘建汀, 温庆放, 朱海生, 李永平. 2025. 普通丝瓜Expansin家族基因的鉴定及其在果实膨大中的表达分析. 园艺学报,2025, 52 (6):1488-1504.
doi: 10.16420/j.issn.0513-353x.2024-0373 |
|
| [4] |
|
| [5] |
doi: 10.1371/journal.pcbi.1009703 URL |
| [6] |
doi: 10.1105/tpc.107.056507 URL |
| [7] |
|
| [8] |
doi: 10.3724/SP.J.1006.2017.01417 |
|
郝心愿, 岳川, 唐湖, 钱文俊, 王玉春, 王璐, 王新超, 杨亚军. 2017. 茶树β-淀粉酶基因CsBAM3的克隆及其响应低温的表达模式. 作物学报, 43 (10):1417-1425.
doi: 10.3724/SP.J.1006.2017.01417 |
|
| [9] |
doi: 10.1038/s41477-018-0287-6 pmid: 30374094 |
| [10] |
|
| [11] |
doi: 10.1046/j.1365-313X.1999.00625.x URL |
| [12] |
|
| [13] |
|
| [14] |
|
| [15] |
doi: 10.1186/s12870-021-02916-8 |
| [16] |
doi: 10.1016/j.jia.2023.07.018 URL |
| [17] |
|
| [18] |
doi: 10.1006/meth.2001.1262 pmid: 11846609 |
| [19] |
doi: 10.1186/s12864-022-08630-5 |
| [20] |
|
| [21] |
doi: 10.1104/pp.114.246421 URL |
| [22] |
|
| [23] |
doi: 10.1111/pce.2014.37.issue-12 URL |
| [24] |
doi: 10.1105/tpc.110.081950 pmid: 21487098 |
| [25] |
doi: 10.1111/jipb.v66.5 URL |
| [26] |
|
| [27] |
doi: 10.1016/j.pbi.2012.03.016 pmid: 22541711 |
| [28] |
|
|
田晓成, 祝令成, 邹晖, 李白云, 马锋旺, 李明军. 2023. 果实可溶性糖的积累模式及其调控研究进展. 园艺学报, 50 (4):885-895.
doi: 10.16420/j.issn.0513-353x.2021-1264 |
|
| [29] |
|
| [30] |
|
|
王成. 2023. 低温对薄皮甜瓜果实膨大期和采后淀粉代谢和糖积累的影响[硕士论文]. 沈阳:沈阳农业大学.
|
|
| [31] |
doi: 10.16420/j.issn.0513-353x.2024-0993 |
|
王心茹, 白帅帅, 孙雨乐, 武欣宇, 曾凤, 刘春英, 张玉喜, 盖树鹏, 袁延超. 2025. ‘凤丹’牡丹PoSnRK基因家族鉴定及其在花衰老中的表达分析. 园艺学报, 52 (9):2363-2376.
doi: 10.16420/j.issn.0513-353x.2024-0993 |
|
| [32] |
doi: 10.1186/s43897-022-00034-z |
| [33] |
|
|
赵粱怡. 2019. 梨β-淀粉酶基因家族生物信息学分析及PbBAM3基因抗寒性鉴定[硕士论文]. 南京: 南京农业大学.
|
| [1] | 陈艺荃, 樊荣辉, 林兵, 陈燕, 吴建设, 钟淮钦. 山茶花花香生物合成相关基因的实时荧光定量PCR内参基因的筛选及验证[J]. 园艺学报, 2026, 53(2): 598-612. |
| [2] | 王艳秋, 班景洁, 曾宇涵, 赖春旺, 黄晓铃, 周建金, 万奎, 赖钟雄, 林玉玲. 多花黄精DREB基因家族鉴定及其在盐胁迫下的响应分析[J]. 园艺学报, 2026, 53(1): 159-173. |
| [3] | 黄伟, 马红叶, 乔荣, 罗孝明, 万明长, 冉俊. 毛花猕猴桃新品种‘贵毛1号’[J]. 园艺学报, 2025, 52(S2): 45-46. |
| [4] | 王宝琛, 罗陈, 闫晋强, 程晓欣, 莫仁连, 刘文睿, 张余洋, 江彪. 冬瓜BhYAB4b基因的克隆、表达及功能研究[J]. 园艺学报, 2025, 52(9): 2353-2362. |
| [5] | 张婷, 王博涛, 张磊, 宋丽华, 曹兵, 马亚平. 宁夏枸杞LbWaxy基因家族鉴定及高浓度CO2处理下的基因表达特征分析[J]. 园艺学报, 2025, 52(9): 2395-2409. |
| [6] | 张拓, 聂梦涵, 刘媛媛, 段昕莲, 韩星, 谢宝贵, 严俊杰. 金针菇过氧化氢酶基因FfCAT1和FfCAT2的表达分析[J]. 园艺学报, 2025, 52(7): 1769-1779. |
| [7] | 杨春梅, 于洋, 丁雨格, 夏京, 周玲, 彭磊. 转录—代谢联合分析‘贵妃’杧果腋芽转化花芽中的淀粉与蔗糖代谢途径[J]. 园艺学报, 2025, 52(6): 1412-1426. |
| [8] | 孙廷珍, 疏琴, 马玮, 史玉滋, 张蒙, 向成钢, 薄凯亮, 段颖, 王长林. 印度南瓜GAox家族基因鉴定及其在不同蔓长种质中的表达[J]. 园艺学报, 2025, 52(3): 603-622. |
| [9] | 邓淑琴, 高莹瑞, 李雨桐, 王瑛, 龚春梅, 白娟. 茶树泛素连接酶基因CsPUB21对非生物胁迫的响应[J]. 园艺学报, 2025, 52(3): 655-670. |
| [10] | 仝宗军, 韩星, 段昕莲, 刘媛媛, 林俊彬, 甘颖, 陈杰, 谢宝贵, 甘炳成, 严俊杰. 金针菇PRX家族基因鉴定及其在子实体发育过程中的表达分析[J]. 园艺学报, 2025, 52(2): 337-348. |
| [11] | 韩宏伟, 常亚南, 刘会芳, 庄红梅, 邢嘉怡, 张晓达, 祖丽皮耶·阿卜杜米力科, 王浩, 王强. 甜瓜细胞色素P450家族基因的鉴定及其响应光辐射强度的表达分析[J]. 园艺学报, 2025, 52(12): 3271-3287. |
| [12] | 柳璐, 王梦, 郑晓美, 王珂青, 苗如意, 臧巧路. 艾草CBF基因家族的鉴定及表达分析[J]. 园艺学报, 2025, 52(10): 2703-2712. |
| [13] | 贺丹丹, 何宏泰, 王文庭, 周文美, 刘燕敏, 刘骕骦. 甜瓜GolS家族基因鉴定及其响应低温胁迫的表达分析[J]. 园艺学报, 2025, 52(1): 136-148. |
| [14] | 郭昌权, 李丹琪, 惠馨冉, 郑婧雅, 侯梦璐, 朱永兴. 姜DUF966基因家族成员鉴定与表达分析[J]. 园艺学报, 2024, 51(9): 2031-2047. |
| [15] | 赵佳莹, 曾周婷, 岑欣颖, 施姣淇, 李效贤, 沈晓霞, 俞振明. 铁皮石斛CCO基因家族鉴定及其在花发育中的表达分析[J]. 园艺学报, 2024, 51(9): 2075-2088. |
| 阅读次数 | ||||||
|
全文 |
|
|||||
|
摘要 |
|
|||||
版权所有 © 2012 《园艺学报》编辑部 京ICP备10030308号-2 国际联网备案号 11010802023439
编辑部地址: 北京市海淀区中关村南大街12号中国农业科学院蔬菜花卉研究所 邮编: 100081
电话: 010-82109523 E-Mail: yuanyixuebao@126.com
技术支持:北京玛格泰克科技发展有限公司